Saúde
Genes que podem explicar por que alguns jovens sauda¡veis ​​desenvolvem sintomas graves de COVID-19
Em seu artigo publicado na revista Science Translational Medicine , o grupo descreve sua análise genanãtica de jovens infectados sem fatores contribuintes conhecidos para a doena§a.
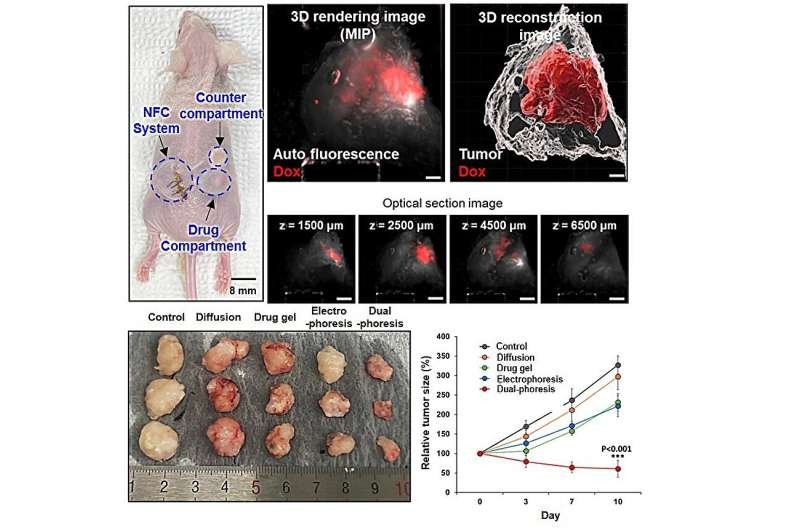
Fig. 1. Uma estratanãgia analatica multi-a´mica identifica os principais caminhos e impulsionadores da Sandrome de Dificuldades Respirata³rias Agudas no COVID-19. (A) Quarenta e sete pacientes craticos (C), 25 pacientes não craticos (NC) e 22 controles sauda¡veis ​​(H) foram incluados no estudo. PBMCs foram isolados por gradiente de densidade e congelados atéa utilização para citometria de massa e protea´mica total. O plasma foi usado para perfis de citocinas e protea´mica total. O soro foi usado para medir anticorpos neutralizantes anti-IFN tipo I, anticorpos neutralizantes anti-SARS-CoV-2 e sorologia antiviral multialvo. Sangue total foi usado para sequenciamento de RNA-seq e genoma completo (WGS). O número de amostras tratadas por grupo e por a´micas éindicado abaixo de cada designação de a´micas. (B) O pipeline de RNA-seq émostrado com base na comparação NC versus C. Para aumentar a robustez das análises downstream, uma abordagem de inteligaªncia de conjunto com sete algoritmos foi aplicada a várias partições dos dados de RNA-seq (consulte Manãtodos) para classificar pacientes NC versus C, realizando análise diferencial em cada partição dos dados. Uma pontuação de classificação de conjunto em seis dos sete algoritmos e todas as partições dos dados foi então determinada, e os 600 principais desses genes foram usados ​​como entrada para a modelagem causal estrutural para derivar uma rede causal putativa. Para apoiar as principais conclusaµes da primeira coorte de pacientes, foram usados ​​dados de RNA-seq de uma segunda coorte de pacientes que consistia em 81 pacientes craticos e 73 pacientes craticos recuperados. Os dados foram particionados analogamente a primeira coorte de pacientes, mas apenas os 600 principais recursos da primeira coorte de pacientes foram usados ​​para avaliar a informatividade da assinatura do gene. (C) Citocinas e células imunes foram quantificadas. Os dados WGS foram usados ​​para análise de eQTL juntamente com as contagens de genes do RNA-seq. Os dados protea´micos foram submetidos a expressão diferencial de proteanas e análises de enriquecimento nGOseq. (D) Os principais caminhos e motivadores resultantes das análises a´micas em (B e C) foram validados em uma segunda coorte de 81 pacientes craticos e 73 pacientes craticos recuperados. A expressão diferencial de ADAM9, o principal gene driver, foi comparada com dados de seq de RNA em massa disponíveis publicamente. Finalmente, experimentos de infecção ex vivo com SARS-CoV-2 foram conduzidos para validar um candidato a gene driver. Crédito: DOI: 10.1126 / scitranslmed.abj7521 Os dados WGS foram usados ​​para análise de eQTL juntamente com as contagens de genes do RNA-seq. Os dados protea´micos foram submetidos a expressão diferencial de proteanas e análises de enriquecimento nGOseq. (D) Os principais caminhos e motivadores resultantes das análises a´micas em (B e C) foram validados em uma segunda coorte de 81 pacientes craticos e 73 pacientes craticos recuperados. A expressão diferencial de ADAM9, o principal gene driver, foi comparada com dados de seq de RNA em massa disponíveis publicamente. Finalmente, experimentos de infecção ex vivo com SARS-CoV-2 foram conduzidos para validar um candidato a gene driver. Crédito: DOI: 10.1126 / scitranslmed.abj7521 Os dados WGS foram usados ​​para análise de eQTL juntamente com as contagens de genes do RNA-seq. Os dados protea´micos foram submetidos a expressão diferencial de proteanas e análises de enriquecimento nGOseq. (D) Os principais caminhos e motivadores resultantes das análises a´micas em (B e C) foram validados em uma segunda coorte de 81 pacientes craticos e 73 pacientes craticos recuperados. A expressão diferencial de ADAM9, o principal gene driver, foi comparada com dados de seq de RNA em massa disponíveis publicamente. Finalmente, experimentos de infecção ex vivo com SARS-CoV-2 foram conduzidos para validar um candidato a gene driver. Crédito: DOI: 10.1126 / scitranslmed.abj7521 (D) Os principais caminhos e motivadores resultantes das análises a´micas em (B e C) foram validados em uma segunda coorte de 81 pacientes craticos e 73 pacientes craticos recuperados. A expressão diferencial de ADAM9, o principal gene driver, foi comparada com dados de seq de RNA em massa disponíveis publicamente. Finalmente, experimentos de infecção ex vivo com SARS-CoV-2 foram conduzidos para validar um candidato a gene driver. Crédito: DOI: 10.1126 / scitranslmed.abj7521 (D) Os principais caminhos e motivadores resultantes das análises a´micas em (B e C) foram validados em uma segunda coorte de 81 pacientes craticos e 73 pacientes craticos recuperados. A expressão diferencial de ADAM9, o principal gene driver, foi comparada com dados de seq de RNA em massa disponíveis publicamente. Finalmente, experimentos de infecção ex vivo com SARS-CoV-2 foram conduzidos para validar um candidato a gene driver. Crédito: DOI: 10.1126 / scitranslmed.abj7521
Uma equipe internacional de pesquisadores isolou cinco genes que são mais ativos em jovens com sintomas graves de COVID-19 do que naqueles com sintomas menos graves. Em seu artigo publicado na revista Science Translational Medicine , o grupo descreve sua análise genanãtica de jovens infectados sem fatores contribuintes conhecidos para a doena§a.
Â
Alguns jovens sauda¡veis , apesar de não terem condições subjacentes aparentes, ainda desenvolvem sintomas de COVID muito graves. Por que isso acontece permanece um mistanãrio. Nesse novo esfora§o, os pesquisadores encontraram uma possível pista - genes que parecem reduzir a capacidade do corpo de lutar contra a doença quando ativados.
O trabalho envolveu a coleta de amostras de plasma de 72 pacientes jovens hospitalizados com COVID, 47 dos quais estavam gravemente enfermos. Nenhum dos participantes da amostra apresentava quaisquer condições subjacentes que pudessem explicar seus sintomas. A equipe também coletou amostras de 22 jovens infectados que apresentavam poucos ou nenhum sintoma para servir de grupo de controle . Os pesquisadores notaram no inicio que os pacientes mais doentes também sofriam de inflamação e coagulação aumentadas. Eles então conduziram o sequenciamento do genoma inteiro nas amostras, junto com o sequenciamento de RNA, protea´mica celular, perfil de citocinas e imunofenotipagem. Eles também usaram um aplicativo de aprendizado de ma¡quina para detectar padraµes nos genes. A análise revelou cinco genes que eram mais ativos nos pacientes com sintomas graves. Um, ADAM9, foi considerado o mais prevalente.
A equipe descobriu que quando o ADAM9 foi bloqueado no tecido pulmonar humano in vitro, o varus foi menos eficiente em se duplicar. Os pesquisadores sugerem que todos os cinco genes que identificaram precisam ser estudados com mais profundidade, particularmente o ADAM9. Isso poderia levar a terapaªutica para desativar a atividade de tais genes e, ao fazaª-lo, reduzir os sintomas de COVID-19.